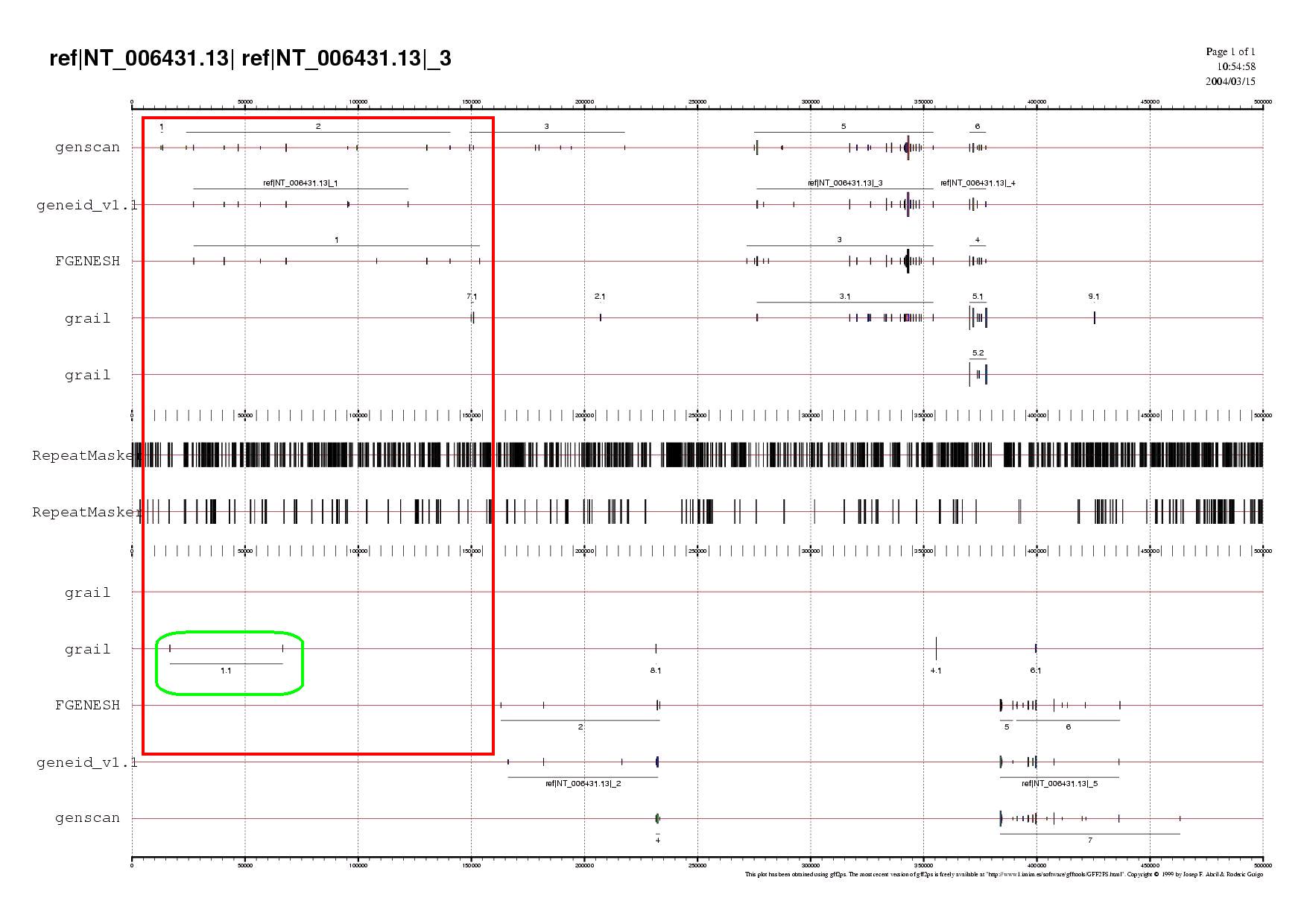
Si cliqueu en aquest link podeu veure un gràfic on hi ha enmarcada la subseqüència 1 en color vermell. En color verd s'han marcat els gens que més tard seran tractats d'identificar.
A la taula següent, que representa les prediccions integrades a la subseqüència A, s'han resaltat amb color vermell l'inici i el final triats.
| PROGRAMA | NÚMERO DE GEN | COORDENADA D' INICI | COORDENADA FINAL | SENTIT |
| Geneid | 1 | 27154 | 122131 | Forward/td> |
| Fgenesh | 1 | 27220 | 153755 | Forward |
| Genscan | 1 | 12744 | 12764 | Forward |
| Genscan | 2 | 23958 | 24050 | Forward |
| Genscan | 3 | 149221 | 149371 | Forward |
| Grail | 1.1 | 66714 | 16764 | Reverse |
| Grail | 7.1 | 149825 | 151077 | Forward |
Validació de la predicció dels gens
A la imatge que apareix a continuació es pot veure la predicció dels gens tan en forward com en reverse i els resultats obtinguts amb el BLASTN.
Es pot observar que de tots els gens predits només en trobem un que estigui suportat pels ESTs, aquest és gen 1 predit pel programa Grail. Les prediccions per la cadena forward no estan suportades per cap ESTs. Aquest resultat sobta bastant perquè tres programes diferents, que no es basaven en homologia, han predit un gen a la cadena forward que no apareix a cap base de dades i que no està suportat.
Ja que el resultat de BLASTN ha donat pocs ESTs s'ha cregut convenient fer un BLASTN per mamífers. Els resultats obtinguts no han estat gaire millors perquè només s'han obtingut dos nous ESTs i aquests no suporten cap dels exons del gen.
Creiem que en aquest cas el millor que es pot fer és no descartar la hipòtesi de l'existència d'aquest gen i intentar esbrinar-ho a través de la cerca del promotor (si n'hi hagués seria indicatiu de una bona predicció de l'exó inicial) i mirar per BLASTP si hi ha homologia amb alguna o algunes proteïnes.
Identificació de les proteïnes
A continuació s'adjunta la seqüència de la proteïna que s'ha fet córrer al programa BLASTP (Grail número 1.1), que estava recolzada pels ESTs.
>GrailEXP Gene 1, Var 1 protein|Derived from similarity to BX089473.1 MLAEPSVRTWMHTQNLHLVISALRGMELERQRSNEAEF*
El programa BLASTP no ha trobat cap proteïna similar o homòloga prou significativa. La conclusió que podem extreure és que o bé aquest gen no ha estat ben predit, o bé és un gen deconegut no homòleg a cap altre ja conegut
La següent proteïna és la predicció 2 de Genscan. S'ha decidit córrer aquest gen perquè havia estat predita per diversos programes.El fet de no trobar ESTs no significa que aquest gen no pugui existir.
>ref|GENSCAN_predicted_peptide_2|450_aa MDLEKLGVCFLEADEYSNDRQWYFLSLYMNQNKTESQSSNWRIDSQSRVRQVIMTTAIPM IKAQPWSRPKPSNPAIFGLQNKRASLFPRFTCEDQGQQLLGVAQSEISNTTFVAVHILNV EHCVLNGISEASSPEEYPTSENTEKGDTEEESSWRESTSIMDATFKTKSQEQDVLPAPRS TMHLKSVLICRNEQLINSLCEVLRLNKCAPLLLPLPQAATLHVPAFERQLRNEAKRDISS FPNPVFKTKHGAAGEIPNTFKPSKAANHKNASHFIFNKFVLYQAYKRNTTVHRDAQIPSS PLFPDLLSKLLPLVHCETSKQTKTLGHEPQTGFPWKGHLPMGLHLPAGSKSAPAALVPSG CAHIINKGTSSANWLHDMDTCPLSIGLELGDFHKGQPTAGRQEPPAPLPHRQPSTSLNSV DPNWTDTRTIQTSLYTRIPPLRPCLDSMSA
Els resultats del BLASTP en aquest cas tampoc han estat significatius.
.gif)
Ens trobem, doncs, davant d'un possible fals positiu perquè és un gen no recolzat per ESTs i sense cap homòleg.
Estudi de les regions promotores
En conseqüència amb els resultats obtinguts anteriorment, s'ha cregut convenient fer únicament l'estudi de el gen predit per programa Grail.
Després de córrer al programa TRANSFAC la possible regió promotora en format fasta, s'ha obtingut el resultat que s'adjunta a continuació:
matrix position core matrix sequence (always the factor name identifier (strand) match match (+)-strand is shown) V$NKX25_02 1 (+) 1.000 1.000 ctTAATTg Nkx2-5 V$CDPCR1_01 117 (-) 0.910 0.937 gcgaTCCATg CDP CR1 V$HAND1E47_01 163 (+) 1.000 0.966 ctatgggTCTGGaagc Hand1/E47 V$EVI1_04 438 (+) 1.000 0.853 agagatgacAAGATg Evi-1
Es prediuen quatre regions promotores, una de les quals (la primera que apareix a la taula) té un molt bon score. Això apunta a l'existència d'aquest gen. De totes maneres, no es pot afirmar contundentment perquè malgrat hi hagi recolzament per ESTs i aquest promotor, els reultats de BLASTP no apuntaven l'existència de cap proteïna homòloga. Seria convenient fer un estudi més exhaustiu per estar-ne segurs.