| DI | eEFSec | GPx | MsrA | SBP2 | Sel15 | SelH | SelI | SelK | SelM | SelN | SelO | SelP | SelR | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| H.sapiens | Sec | N/A | UC | Cys | N/A | Sec | Sec | Sec | Sec | Sec | Sec | Sec | Sec | U/C |
| T.brucei | X | H | C | C | X | X | X | X | U | X | X | X | X | C |
| SelS | SelT | SelU | SelV | SelW | SPS | TR | |
|---|---|---|---|---|---|---|---|
| H.sapiens | Sec | Sec | Cys | Sec | U/C | U/T | Sec |
| T.brucei | X | U | C | X | X | C | X |
X = Proteína no presente en T.brucei
U = Proteína homóloga con selenocisteína
C = Proteína homóloga con cisteína
H = Proteína homóloga con otros aminoácidos
Al igual que con la búsqueda de selenoproteínas homólogas, mediante el TBLASTN se encontraron dos posibles homologías: eEFSec y SPS.
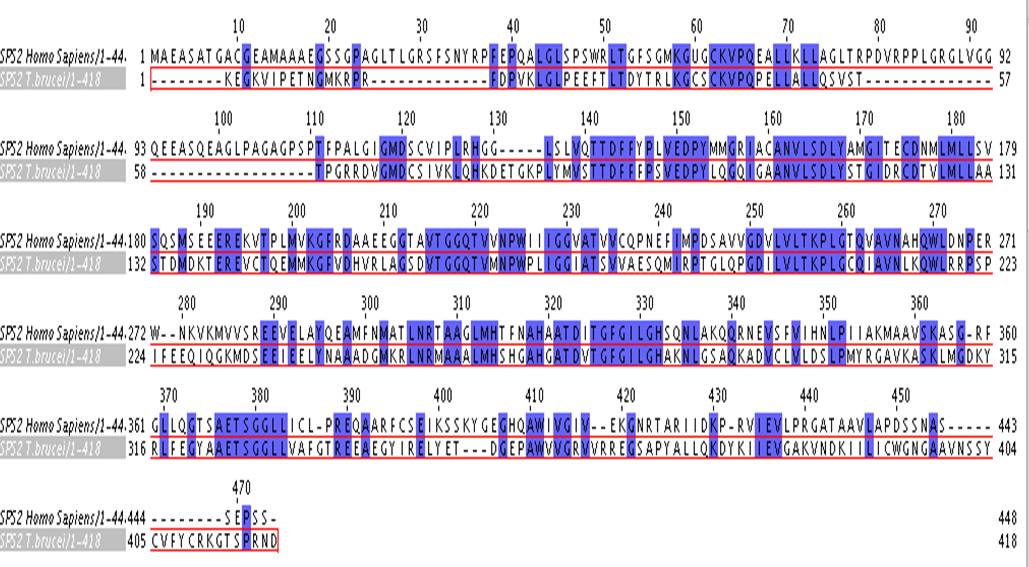
La proteína humana SBP2 (SECIS-Binding Protein), implicada en la incorporación de Sec, no está presente en el genoma de T. brucei: En primer lugar porque al realizar el TBLASTN, el hit con un e-value más pequeño era de 2'3, pero para asegurar que no existía ninguna proteína homóloga, se realizó un alineamiento local con el programa Exonerate y no se obtuvo ningún resultado. En el caso de eEFSec (factor de elongancioacute;n específico para Sec), se encontró un hit con un e-value de 9*10-82, por lo tanto se continuó con el análisis. El alineamiento realizado con el programa GeneWise no fue significativo, así que se utilizó el programa Exonerate, y realizando unos pequeños ajustes comentados en el apartado Materiales y Métodos, se logró obtener un buen alineamiento. El resultado obtenido con T-Coffee era correcto, excepto al final de la secuencia, que presentó muchos gaps. La solución consistió en hacer el alineamiento global sólo con la parte de la secuencia que se alineaba con Exonerate. De esta forma, se obtuvo un buen alineamiento de la proteína eEFSec humana y la homóloga en T.brucei. El resultado es el siguiente: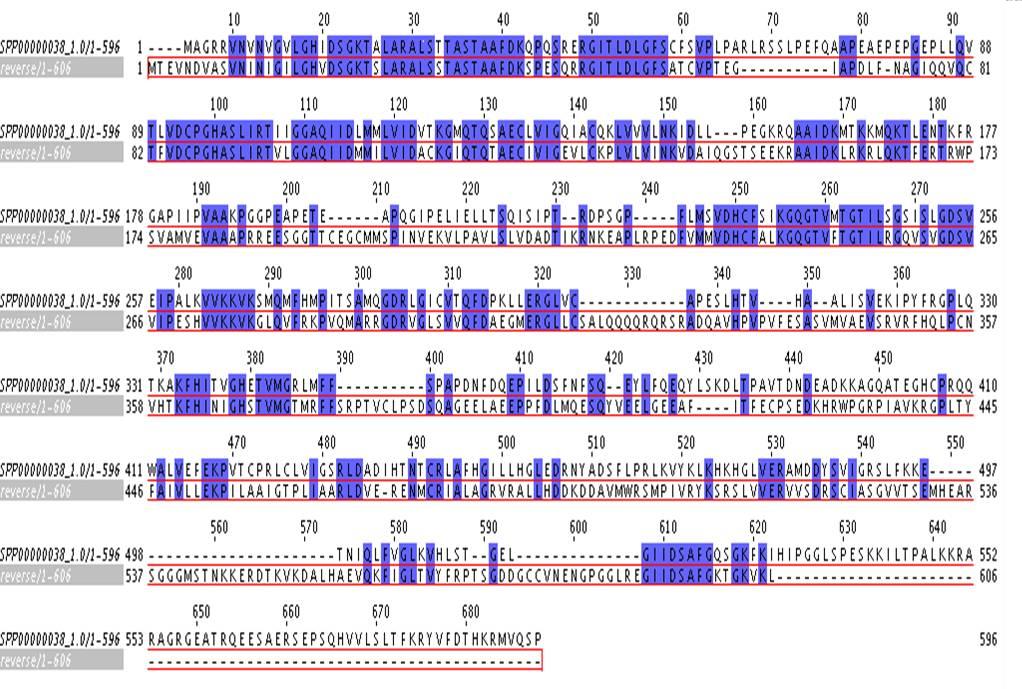 De las proteínas de la família SPS (SPS1 y SPS2) de Homo sapiens, en T. brucei sólo se encuentra un homólogo. Se trata de enzimas (SelenoPhosphate Synthetases) implicadas en la generación del donador de selenio, monoselenofosfato, necesario para la biosíntesis de Sec.
Al realizar el primer alineamiento con TBLASTN, con SPS1 y con SPS2, el resultado mostraba la misma región. En cada caso, había hits con e-value bajo (4*10-77 y 6*10-64, respectivamente). Debido a que el raw score del alineamiento de la SPS2 era ligeramente superior al de la SPS1, se continuaron los análisis con esta subsecuencia de T. brucei. El resultado final con el T-Coffee es el siguiente:
De las proteínas de la família SPS (SPS1 y SPS2) de Homo sapiens, en T. brucei sólo se encuentra un homólogo. Se trata de enzimas (SelenoPhosphate Synthetases) implicadas en la generación del donador de selenio, monoselenofosfato, necesario para la biosíntesis de Sec.
Al realizar el primer alineamiento con TBLASTN, con SPS1 y con SPS2, el resultado mostraba la misma región. En cada caso, había hits con e-value bajo (4*10-77 y 6*10-64, respectivamente). Debido a que el raw score del alineamiento de la SPS2 era ligeramente superior al de la SPS1, se continuaron los análisis con esta subsecuencia de T. brucei. El resultado final con el T-Coffee es el siguiente:Estos resultados no implican que no puedan existir otros tipos de proteínas necesarias para la síntesis de selenoproteínas en el genoma de T. brucei, pero sí se podría afirmar que eEFSec y SPS2 son las únicas proteínas de maquinária homólogas al genoma de H. sapiens. Futuros estudios podrín ir encaminados hacia el descubrimiento de nuevas proteínas propias de T. brucei implicadas en la biosíntesis de selenoproteínas.
Otros alineamientos con GeneWise en el terminal tampoco mostraron una mejoría en cuanto a los alineamientos, por lo que se procedió a analizar la secuencia manualmente para verificar la presencia de un codón TGA in frame seguido de un codón STOP, obteniendo los siguientes resultados:

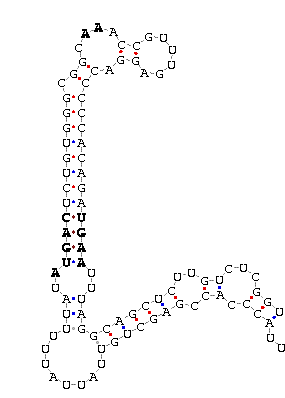
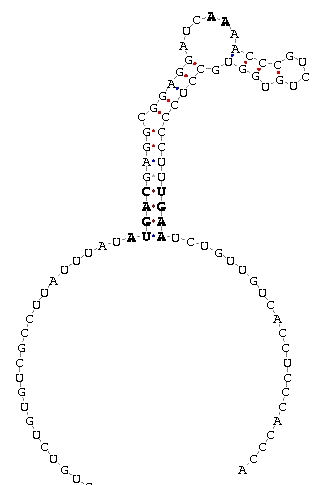
Con el SECISearch se observó la presencia de un elemento SECIS, cuyo COVE score era de 17.78.

El resultado de la construcción del cladograma con ClustalW muestra una mayor similitud entre la SelK de H. sapiens y la de T. brucei, respecto a SelK de A. gambiae y los homólogos con cisteína de C. elegans y D. melanogaster:
 En el caso de SelT, se consiguió alinear la selenoproteína humana SelT con el genoma de T. brucei mediante el TBLASTN y se eligió la subsecuencia con el e-value más bajo, de 3*10-6 (Tb927_05_v4:subseq(294000,1500)). Como resultado de alinear esta subsecuencia con la secuencia proteica de la SelT humana en el GeneWise, se alineó la selenocisteína de SelT con un codón STOP del genoma de nuestro organismo. Entonces se halló este codón en el genoma de T. brucei y se corroboró que se trataba de una seleocisteína ya que contenía los nucleótidos TGA para este codón. Con la ayuda de la SelT humana y del alineamiento obtenido en GeneWise se pudo predecir la secuencia nucleotídica de SelT en el organismo de estudio mediante la búsqueda de la metionina inicial y el siguiente codón STOP.
En el caso de SelT, se consiguió alinear la selenoproteína humana SelT con el genoma de T. brucei mediante el TBLASTN y se eligió la subsecuencia con el e-value más bajo, de 3*10-6 (Tb927_05_v4:subseq(294000,1500)). Como resultado de alinear esta subsecuencia con la secuencia proteica de la SelT humana en el GeneWise, se alineó la selenocisteína de SelT con un codón STOP del genoma de nuestro organismo. Entonces se halló este codón en el genoma de T. brucei y se corroboró que se trataba de una seleocisteína ya que contenía los nucleótidos TGA para este codón. Con la ayuda de la SelT humana y del alineamiento obtenido en GeneWise se pudo predecir la secuencia nucleotídica de SelT en el organismo de estudio mediante la búsqueda de la metionina inicial y el siguiente codón STOP.

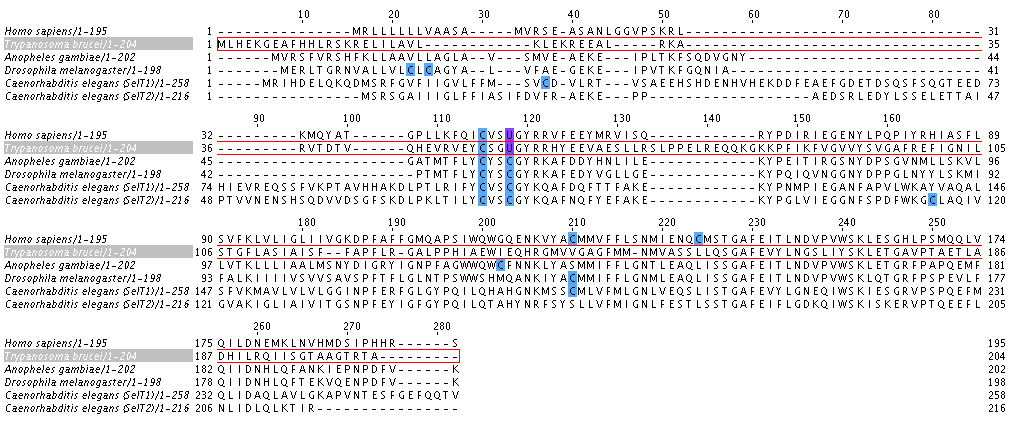
Además se usó el programa T-Coffee para realizar el alineamiento múltiple de las secuencias proteicas de SelT de Homo sapiens,Drosophila melanogaster, Anopheles gambiae y Caenorhabditis elegans con la predicha para T.brucei y el resultado se muestra en la siguiente figura. Como podemos ver, hay correlación de selenocisteína de T.brucei con H. sapiens y el resto de organismos són homólogos en cisteína.
La familia GPx está formada por ocho proteínas, de las cuales la 5, la 7 y la 8 son homólogas con cisteína de la propia familia (no existen como selenoproteínas en ninguna otra especie). La relación evolutiva entre la familia se muestra en la siguiente figura.
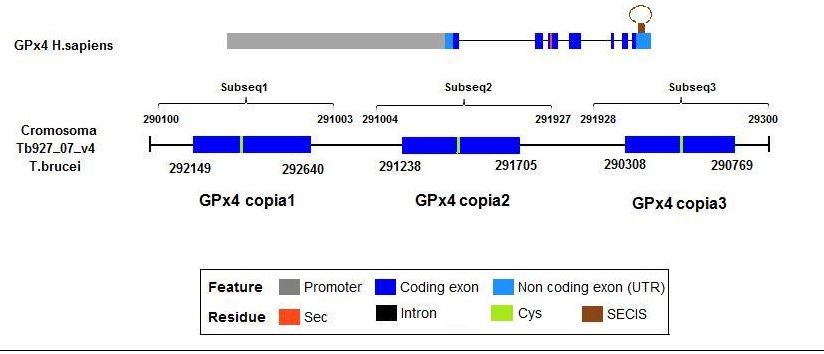
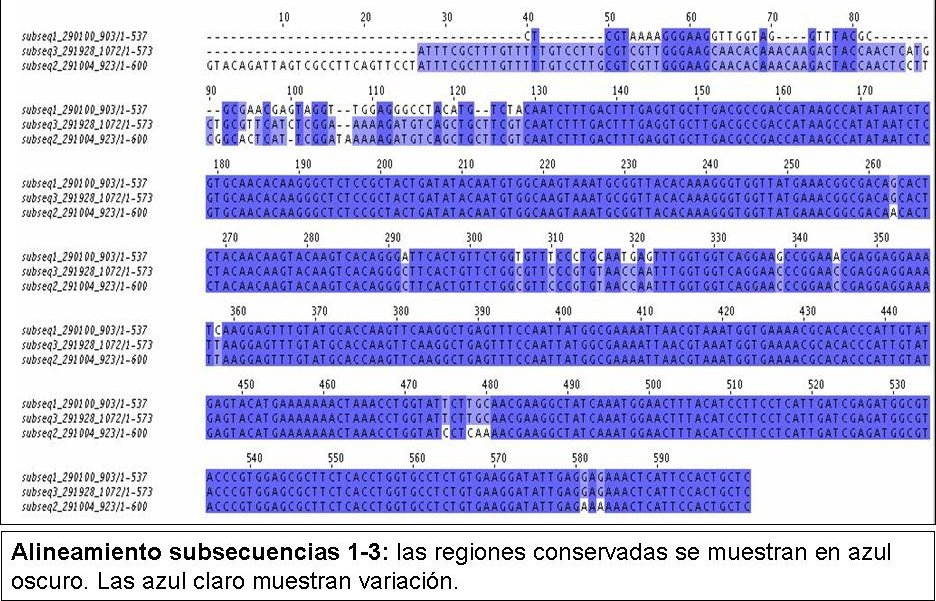
En el genoma del Trypanosoma se encontró que todas estas proteínas se alinearon en la misma región del genoma. Los mejores hits se dieron en Gpx4 y Gpx7. En el caso de la Gpx4 encontramos tres hits importantes en la misma región. Al analizar las regiones más detalladamente, se sospechó que podría tratarse de una duplicación del gen. Para comprobarlo se cortaron 3 subsecuencias no solapantes que abarcaron cada hit (subsecuencia1-3). Seguidamente se hizo la predición de GPx4 en cada subsecuencia. Se hizo lo mismo con el Geneid pero como no aportaba información nueva nos quedamos con la predicción de GeneWise. Con las secuencias predichas se hizo un alineamiento múltiple con el programa T-Coffee. El resultado se muestra en la siguiente imagen en la cual podemos comprobar que realmente se trata de una triplicación del gen que codifica para la GPx4 en el cromosoma 4 del T.brucei.
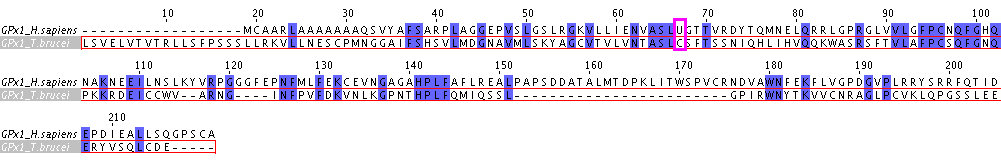
En el caso de la Gpx7, al ser una homóloga con cisteína, se pasó a analizar el siguiente hit más importante, el de GPx1. La predicción del GeneWise no coincidió con el alineamiento inicial del TBLASTN. Por ello se analizaron las todas la posibles pautas de lectura de la subsecuencia y, de aquella que contenía la proteína antes alineada con el Blast, se extrajo la secuencia de ésta. En el alineamiento de la proteína extraída con la GPx1 , la selenocisteína de la GPx1 se alineó con una cisteína, por tanto se trata de una homóloga con cisteína.
El TBLASTN de SelI de H. sapiens contra el genoma de T. brucei dio como resultado un alineamiento con un e-value de 8*10-25con una subsecuencia del cromosoma 10 (Tb927_10_v4: subsecuencia(2165082,3000)).
Los resultados de GeneWise del alineamiento de dicha subsecuencia con SelI mostraron un alineamiento perfecto en un pequeño fragmento de la secuencia. El alineamiento de la selenocisteína de SelI con un codón TGA o con una cisteína fue imposible de realizar, por lo que suponemos que T. brucei no presentaría un homólogo a SelI.
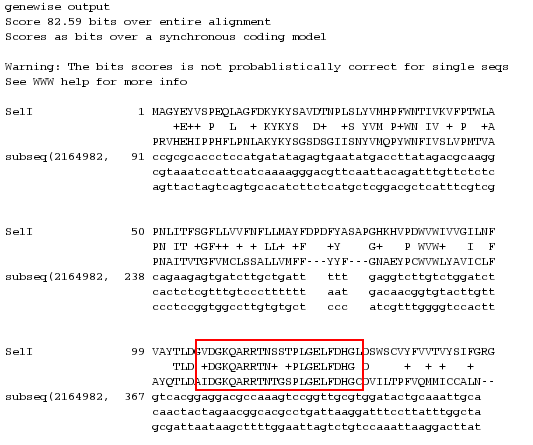
Puesto que sí que se consiguió un alineamiento parcial de la secuencia, pensamos que podría deberse a un dominio funcional común en SelI y una proteína de T. brucei. Para ello introducimos la secuencia proteica de T. brucei en Prosite. El resultado obtenido fue que el dominio DGKQARRTNTGSPLGELFDHGCD corresponde al patrón que se encuentra en las alcohol phosphatidyltransferases.
La selenoproteína SelI se encuentra únicamente en H. sapiens y su función corresponde a una ethanolaminephosphotransferase, de modo que T. brucei podría presentar este dominio en alguna de sus proteínas.
El rastreado de SECIS en el genoma dio un total de 77 posibles SECIS. De todos estos sólo 22 tenían un COVE score mayor a 8 y fueron las secuencias de estos las que se utilizaron en el BLASTN.
La siguiente tabla resume los resultados del BLASTN, para cada secuencia se eligió el mejor hit según los parámetros descritos arriba.
La búsqueda de posibles selenoproteínas se restringió a los hits resaltados en negrita en la tabla anterior, que son los que corresponden a los SECIS que presentaron un COVE score mayor a 15. Sus principales características se muestran en la siguiente tabla:En estos cuatro casos se realizó el procedimiento completo arriba explicado para predecir las nuevas selenoproteínas potenciales.
Posible selenoproteína (31 aa.):
MLRSTUAICSAGDHLSLMTSRQMRPNLSTLG
En la subsecuencia del SECIS 26 se encontraron dos posibles selenoproteínas, cada una está en una pauta de lectura diferente, ambas en la cadena positiva. El SECIS identificado es válido para las dos.
Posible selenoproteína 1 (35 aa.):
MVKKEYIITFUKVVKNEYMFFFGFNTLFCVYERNK
Posible selenoproteína 2 (69 aa.):
MVVRTSFYVPLSLFIFTSCTLILLAMPSILCLWWRSCGLPVRLLRWLIPLVEDG UWCRSQAPLLDTGTN
En la subsecuencia del SECIS 30 se encontraron dos posibles selenoproteínas en la secuencia reversa complementaria a la subsecuencia. A pesar que el codón STOP in frame fuese un TGA vimos que no podían ser selenoproteínas porque no se encontraba un SECIS dentro de la misma subsecuencia.
En el caso del SECIS 30 se alineó perfectamente en dos regiones diferentes en el cromosoma XI, la primera subsecuencia presentó dos posibles selenoproteínas con un TGA in frame pero, al igual que el anterior, se encontraban en la secuencia reversa complementaria y no presentaban el SECIS dentro de la misma subsecuencia.
De las tres posibles selenoproteínas, sólo en una el codón STOP es un TGA y presenta el SECIS.
Posible selenoproteína (69 aa.):
MSCCMRCTGSRREWLVFIISDVNSFFFFFWCVTVGYGDYVRPMTWLLPSCWDE UCSRCRMFFLWEEEVGLas cuatro subsecuencias se presentan en el siguiente pdf, indicando en amarillo la secuencia codificante de la proteína, en rojo el codón TGA correspondiente a la selenocisteína, en azul el TGA final, en verde se muestran los SECIS y dentro de los SECIS en rojo se muestran los nucleótidos que posteriormente darán lugar principalmente a la estructura secundaria de los SECIS.
Secuencias (pdf)| <- Mat. y Met. | Homólogas | GPx | Nuevas | Conclusiones -> |